Introduction
Materials and Methods
공시데이터
SNP quality control 및 genotypes filtering
Principal component analysis
ADMIXTURE analysis
Results and Discussion
국내 한우, 홀스타인, 저지 집단의 유전적 구조 및 혼합도(admixture) 분석
홀스타인과 저지 집단 간 유전적 분리도 및 유전적 조성 평가
교잡(F1 - F6) 세대를 포함한 유전적 구조 분석 및 유전적 조성 평가
Conclusion
Introduction
저지(Jersey) 품종은 홀스타인(Holstein) 품종에 비해 상대적으로 작은 체구와 높은 사료효율을 바탕으로 고형분 비율이 높은 우유를 생산하는 것으로 알려져 있으며(Aikman et al., 2008), 최근 기후 환경 변화에 따른 내서성(heat tolerance) 측면에서도 주목받고 있다(Lim, 2020; 2021). 국내에서는 젖소 품종 수입 규제가 완화된 2010년 이후 본격적으로 도입되었으며, 2014년 유대 산정 체계에 유단백질 비율이 포함되면서 산업적 관심이 증가하였다. 반면, 국내 주요 품종인 홀스타인은 장기간 고유량 개량이 이루어지면서 번식력 저하 등 기능형질의 약화가 문제로 제기되어 왔다(Royal et al., 2000). 이에 따라 교잡육종(crossbreeding)은 유성분 개선 및 번식성 향상이라는 장점으로 인해 활용도가 증가하고 있으며, 특히 홀스타인 × 저지 교잡은 실용적 대안으로 보고되고 있다(McAllister, 2002; Heins et al., 2008).
홀스타인과 저지를 교잡한 F1 세대는 홀스타인 수준의 유량과 저지와 유사한 유성분 특성을 나타내며, 초기 교배에서 수정률이 높다는 보고도 있다(Heins et al., 2008). 일반적으로 홀스타인에 저지를 반복적으로 교배(backcross)할 경우, 약 7세대에 걸쳐 누적 교배가 진행되어야 유전적으로 약 99% 수준의 저지 품종과 유사한 자손이 형성되는 것으로 알려져 있다. 초기 세대(F1 - F3)의 자손은 홀스타인과 저지의 유전적 구성이 혼재되어 있어, 모색과 주요 형질에서 두 품종의 중간적 특성을 나타낸다. 그러나 이러한 누적 교배는 형질적으로 저지와 유사한 표현형을 보이더라도, 실제 유전적 구성은 세대별로 상이하며, 국가 차원의 혈통 등록 및 품종 관리 체계에서는 이러한 F세대 교잡우를 어떠한 기준으로 저지 품종으로 분류할 지에 대한 명확한 지침이 부재한 상황이다. 특히 품종 구분을 위한 객관적 근거가 주로 외모, 색소, 개량 이력 등에 의존하고 있어, 교잡 세대의 실제 유전적 조성(genetic ancestry)을 반영하지 못한다는 한계가 존재한다.
따라서 본 연구에서는 저지, 홀스타인, 한우의 유전적 구성을 고밀도 SNP 데이터를 통해 비교·분석하고, 이를 reference 데이터로 활용하여 홀스타인에 저지를 누적 교배하여 생산된 F1 - F6 교잡 세대의 유전적 조성이 세대별로 어떻게 변화하는지 정량적으로 평가하고자 하였다. 궁극적으로는 누적 교배가 몇 세대 진행되었을 때 유전적으로 저지 품종에 해당한다고 판단할 수 있는지에 대한 기준을 제시함으로써, 국내 젖소 품종 등록 체계의 과학적 타당성을 높이고 유전자원 관리 및 품종 보존 전략 수립에 기여하고자 한다.
Materials and Methods
공시데이터
한우, 홀스타인, 저지 품종을 비교하는 첫 번째 분석에 사용된 개체들은 국내에서 사육 중인 한우 1,994두, 홀스타인 1,919두, 저지 품종 630두로 총 3,643이다. 이 집단에서 홀스타인, 저지 품종을 reference data로 이용하기 위해 품질관리(quality control, QC) 과정을 거쳐 저지 품종은 494두, 홀스타인 품종은 742두와 F 세대(F1 - F6) 98두, 총 1,334두를 두 번째 분석에 사용하였다. 사용된 교잡 세대는 저지와 홀스타인 1대 1로 교배하여 태어난 F1 개체에 저지를 누진교배 하였으며 6세대까지 같은 방식으로 진행되었다.
SNP quality control 및 genotypes filtering
Illumina BovineSNP50 v3 chip으로부터 얻은 유전자형 데이터에 대해 분석 신뢰도를 확보하기 위한 품질관리(QC)를 수행하였다. 전체 SNP 중 결측률이 10%를 초과하는 변이(--geno 0.1)와 개체별 결측률이 10% 이상인 시료(--mind 0.1)는 분석에서 제외하였다. 또한 최소 대립유전자 빈도(minor allele frequency, MAF)가 0.01 미만(--maf 0.01)이거나 Hardy–Weinberg 평형검정(Hardy–Weinberg equilibrium, HWE)에서 p < 1 × 10-6 (--hwe 0.000001)으로 유의하게 이탈한 SNP도 제거하였다. 이러한 QC 절차는 대규모 집단유전학 연구에서 일반적으로 활용되는 표준 기준(Anderson et al., 2010; Marees et al., 2018)을 바탕으로 하였으며, 모든 분석은 PLINK v1.9 (Purcell et al., 2007)를 이용하여 수행하였다. QC를 통과한 SNP는 두 단계의 분석에 구분하여 활용하였다. 한우·홀스타인·저지 세 품종의 집단 구조 평가에는 총 47,450개의 SNP가 사용되었으며, 홀스타인과 저지 reference 집단 및 F1 - F6 교잡 세대 비교 분석에는 동일 QC 기준을 충족하고 두 품종에서 공통적으로 존재하는 26,931개의 SNP를 최종적으로 사용하였다.
Principal component analysis
주성분분석(principal component analysis, PCA)은 품종 간 집단 구조를 평가하고 개체 간 유전적 분산 패턴을 시각적으로 확인하기 위해 수행하였다. PCA는 고차원의 유전자형 데이터를 저차원 공간으로 축소하여 주요 변이를 설명하는 주성분을 도출하며, 이를 통해 홀스타인과 저지 집단 간 유전적 거리 및 분리 여부를 정량적으로 비교할 수 있다. 본 연구에서는 QC를 완료한 SNP 데이터를 바탕으로 PLINK v1.9 (Purcell et al., 2007)의 기본 PCA 알고리즘을 이용하여 분석을 수행하였으며, 상위 주성분(PC1 - PC2)을 활용하여 집단 분포와 유전적 구조의 차이를 시각화 하였다.
ADMIXTURE analysis
홀스타인과 저지 집단의 유전적 조성(reference ancestry)을 기반으로 교잡 세대(F1 - F6)의 품종별 유전 비율을 추정하기 위해 ADMIXTURE v1.3.0 (Alexander et al., 2009; Alexander and Lange, 2011)을 사용하여 supervised ancestry 분석을 수행하였다. ADMIXTURE 분석에 필요한 입력 파일은 PLINK v1.09 (Purcell et al., 2007)를 이용하여 생성하였다. Reference population은 PCA 및 QC 결과를 바탕으로 각 품종 고유 ancestry 비율이 99% 이상인 홀스타인 및 저지 개체로 구성하였으며, 이 reference 집단을 기준으로 교잡 세대의 ancestry 비율을 추정하였다. Supervised 모드에서 K = 2로 설정한 이유는 분석 대상이 홀스타인과 저지 두 품종이며, 이들 두 집단의 유전적 구성 비율을 기반으로 교잡 세대의 ancestry를 추정하기 위함이다. ADMIXTURE는 각 개체의 품종별 ancestry 비율을 0 - 1의 범위로 출력하며, 본 연구에서는 이를 활용하여 F1 - F6 교잡 세대의 세대가 진행됨에 따라 홀스타인과 저지 유전 구성비가 어떻게 변화하는지를 정량적으로 평가하였다.
Results and Discussion
국내 한우, 홀스타인, 저지 집단의 유전적 구조 및 혼합도(admixture) 분석
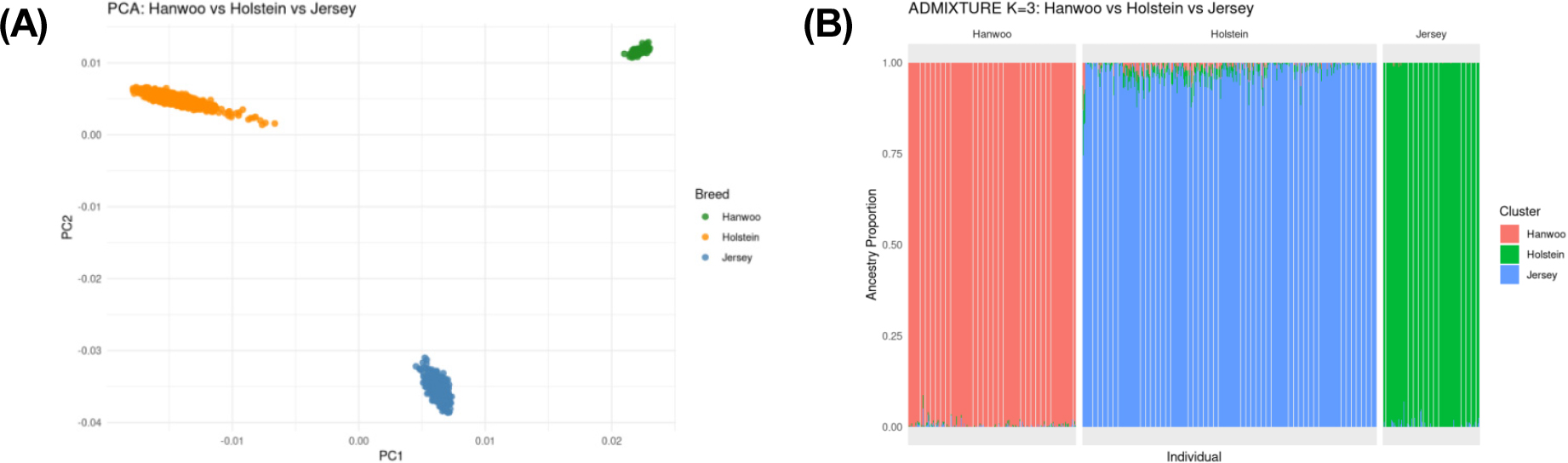
총 3,643두(한우 1,994두, 홀스타인 1,919두, 저지 630두)와 47,450개의 QC-filtered SNP을 이용하여 PCA를 수행한 결과, PC1과 PC2는 각각 전체 유전적 변이의 52.3%와 37.5%를 설명하였으며, 두 주성분의 누적 설명력은 89.8%에 달하였다(Fig. 1A). PCA 산점도에서 세 품종은 명확히 구분되는 세 개의 독립된 군집을 형성하였으며, 특히 PC1 축에서 한우와 유럽계 젖소(홀스타인·저지)가 강하게 분리되었고, PC2 축에서는 홀스타인과 저지가 뚜렷이 구분되었다. 이는 세 품종 간 유전적 혼합이 거의 없음을 시각적으로 확인한 결과로, 집단 간 구조적 차이가 크다는 것을 보여준다.
또한, 세 품종(한우, 홀스타인, 저지) 간 유전적 혼합도와 집단 구조를 정량적으로 평가하기 위해 ADMIXTURE 분석(K = 3)을 수행하였으며, 동일한 경향이 관찰되었다. 분석 결과, 세 품종은 각기 고유한 군집을 형성하였으며, 군집 간 혼합 비율은 매우 낮게 나타났다(Table 1; Fig. 1B). 한우는 군집 1에서 평균 0.995 (99.52%), 홀스타인은 군집 2에서 0.976 (97.58%), 저지는 군집 3에서 0.996 (99.59%)의 ancestry proportion을 보여, 세 품종 모두에서 주요 조상 기여도가 각각 고유 품종으로 명확히 구분됨을 확인하였다. 이는 세 품종 간 유전적 혼합(admixture)이 거의 없으며, 독립적인 품종 구조를 유지하고 있음을 의미한다. 개체 수준 ancestry proportion을 나타낸 Fig. 1B에서도, 한우·홀스타인·저지 개체는 각기 고유한 색상 군집으로 분리되어 나타났으며, 불순도(admixed individuals)는 거의 관찰되지 않았다.
결론적으로, 세 품종은 확연하게 분리된 집단 구조를 형성하였으며, 이는 기존 국내·외 연구에서 보고된 품종 간 유전적 차이 및 고유성 유지 경향과 일치한다(Lee et al., 2016).
Table 1.
Composition ratios of Hanwoo, Holstein, and Jersey breeds estimated using ADMIXTURE analysis (K = 3).
| Breed | Cluster 1 | Cluster 2 | Cluster 3 |
| Hanwoo | 0.9952 | 0.0025 | 0.0022 |
| Holstein | 0.0087 | 0.0156 | 0.9758 |
| Jersey | 0.0004 | 0.9958 | 0.0038 |
홀스타인과 저지 집단 간 유전적 분리도 및 유전적 조성 평가
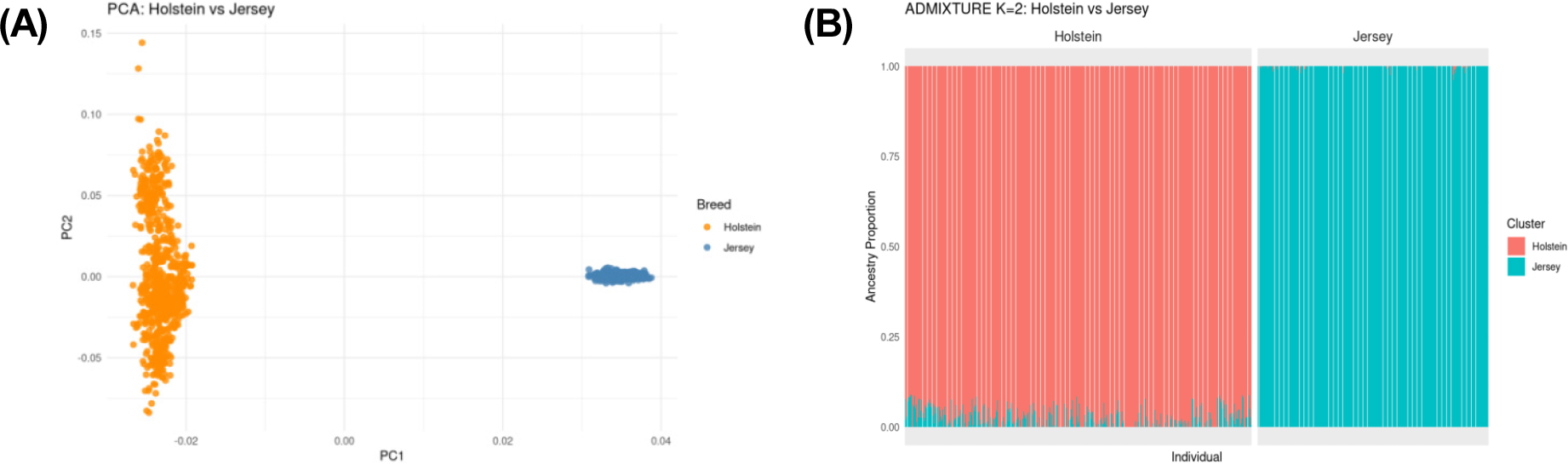
한우를 제외한 전체 개체 중에서 유전적 순수도(genetic purity) 0.99 이상을 만족하는 개체만을 선별하여 홀스타인(742두)과 저지(494두) 집단을 구성한 후, 총 1,236두와 26,931개 SNP 마커를 이용하여 주성분분석(PCA)을 수행하였다. 분석 결과, 제1주성분(PC1)은 전체 유전적 변이의 35.3%, 제2주성분(PC2)은 7.3%를 설명하였으며, 누적 설명력은 42.6%로 나타났다. Fig. 2A에 제시된 PCA 결과에서, 홀스타인과 저지 개체들은 두 개의 명확히 분리된 클러스터를 형성하였으며, 두 집단 간 중첩(overlap)은 전혀 관찰되지 않았다. 이는 유전적 순수도 기준(≥ 0.99)이 집단 내 불순도(individual admixture)를 효과적으로 제거하였으며, 두 품종 간에 명백하고 강한 유전적 차이가 존재함을 보여준다. 또한, PCA 설명력이 한우·홀스타인·저지 세 품종을 모두 포함한 분석(89.8%)보다 낮게 나타난 것은, 비교 대상이 두 집단으로 제한되고 SNP 수가 감소한 데 따른 자연스러운 현상으로 판단된다. 종합적으로, 본 분석은 홀스타인과 저지가 완전히 구분되는 독립적 유전 집단임을 정량적으로 확인하였으며, 이후 유전체 평가 및 참조집단(reference population) 구축 과정에서 두 품종을 분리하여 다루는 것이 타당함을 시사한다.
홀스타인과 저지 reference 집단에 F1 - F6 교잡 세대를 포함하여 유전적 혼합도를 평가하기 위해, 유전적 순수도 0.99 이상을 만족하는 홀스타인 및 저지 개체만을 reference로 선정한 뒤 ADMIXTURE 분석(K = 2)을 수행하였다. 분석 결과, reference 집단인 홀스타인은 평균 97.90%, 저지는 99.88%의 높은 조상 비율(ancestry proportion)을 나타내어, 두 품종이 유전적으로 거의 순수한 독립 집단임을 확인하였다(Table 2). Fig. 2B에서 볼 수 있듯이, 홀스타인과 저지는 두 개의 조상 집단(cluster)으로 명확하게 분리되었으며, reference 개체들 간 혼합(admixture)은 거의 관찰되지 않았다. 이는 앞선 PCA 분석에서 확인된 두 품종 간 뚜렷한 분리 구조와 일치하는 결과로, 본 연구에서 선정한 reference data가 안정된 품종 대표집단으로 기능함을 시사한다.
Table 2.
Genetic composition ratios of Holstein and Jersey reference populations estimated using supervised ADMIXTURE analysis (K = 2).
| Breed | Cluster 1 | Cluster 2 |
| Holstein | 0.0210 | 0.9790 |
| Jersey | 0.9989 | 0.0011 |
본 연구에서 확인된 홀스타인과 저지 reference 집단의 독립적 분리 구조는 국제적으로 보고된 유사 연구 결과와도 일치한다. 예를 들어, Goli 등(2025)은 인도 교잡 젖소 집단에서 locus-specific ancestry 분석을 통해, 교잡 개체에서도 모계·부계 조상에 따른 뚜렷한 분리가 나타나며, reference 집단과의 비교를 통해 교잡 후대의 유전적 혼합 수준을 정량화 할 수 있음을 보고하였다. 또한, Strucken 등(2021)은 소규모 SNP 패널을 활용하여 인도 교잡 젖소의 품종 비율을 추정할 때, reference 집단(순수 Holstein, Jersey 등)과 교잡 세대 간 명확한 구분이 가능하였으며, 이를 기반으로 교배 계획과 유전적 관리 전략을 수립할 수 있음을 제시하였다.
이러한 선행 연구 결과와 본 연구의 PCA 및 ADMIXTURE 분석 결과를 종합하면, 홀스타인과 저지 reference 집단의 유전적 독립성 및 순수도는 국제적 패턴과 일치하며, 본 연구에서 선정한 reference data가 국내 교잡 젖소의 유전 평가 및 후속 연구에서 안정적인 기준으로 활용될 수 있음을 뒷받침한다. 특히, 명확한 reference 집단 구분은 이후 F1 - F6 교잡 세대에서 각 세대별 혼합 비율을 추정하고, 교배 구조에 따른 유전 조성의 변화 양상을 해석하는 데 중요한 기준선을 제공한다. 즉, reference 집단이 두 품종을 완전히 구분해주기 때문에, F세대 자손이 어느 시점부터 특정 품종(예: 저지)과 유전적으로 유사해지는지 평가하는 것이 가능하다.
교잡(F1 - F6) 세대를 포함한 유전적 구조 분석 및 유전적 조성 평가
홀스타인과 저지 reference 집단에 F1 - F6 교잡 세대를 포함하여 유전적 구조를 평가하기 위해 PCA를 수행하였으며, 그 결과는 Fig. 3A에 제시하였다. 분석에는 기구축된 홀스타인 및 저지의 reference 집단 1,236두와 F1 - F6 교잡 세대 98두에 대한 26,931개 SNP 마커가 사용되었다. 제1주성분(PC1)과 제2주성분(PC2)은 각각 전체 유전적 변이의 52.6%와 10.0%를 설명하여, 누적 설명력은 62.6%로 나타났다. PC1은 홀스타인과 저지 reference 집단을 명확하게 구분하는 주요 축으로 작용하였으며, 모든 개체가 두 품종 사이에서 뚜렷하게 분리된 분포를 보였다. 교잡 세대(F1 - F6)는 PC1 상에서 두 품종 사이에 점진적으로 배열된 형태의 연속적(gradient) 분포를 보였으며, 이를 통해 각 세대가 지닌 유전적 혼합 정도를 시각적으로 확인할 수 있었다. 특히, F1 - F2는 두 reference 집단의 중간 위치에 군집하는 경향을 보였고, 세대가 진행됨에 따라(F3 - F6) 저지 집단에 점차 가까워지는 방향으로 이동하는 분포 패턴이 관찰되었다. 이러한 결과는 교잡 세대가 누적될수록 저지 품종 유전체 기여도가 증가함을 반영하며, 또한 reference 집단과의 상대적 위치를 기반으로, F세대 후손을 어느 시점에서 저지 품종으로 분류할 수 있는지 평가하는 기초 자료로 활용 가능하다.
홀스타인과 저지를 기준 조상(reference ancestry)으로 설정하여 F1 - F6 교잡 세대의 유전적 혼합도를 평가하기 위해 supervised ADMIXTURE 분석(K = 2)을 수행하였다. Reference 집단은 유전적 순수도 ≥ 0.99 기준을 충족하는 개체만을 포함하여 구성하였으며, 이를 통해 F세대 조성 추정의 정확성을 높였다. 분석 결과, F세대가 진행됨에 따라 저지 ancestry proportion이 점진적으로 증가하는 뚜렷한 패턴이 관찰되었다(Table 3; Fig. 3B). F1 세대는 홀스타인 44.8%, 저지 55.2%의 혼합 조성을 보였으며, F2 세대는 저지 비율이 74.1%로 증가하여 초기 교배 효과가 반영됨을 확인하였다. F3 세대에서는 저지 비율이 87.0%로 상승하여, 저지 조성의 우세가 더욱 강화되었다.
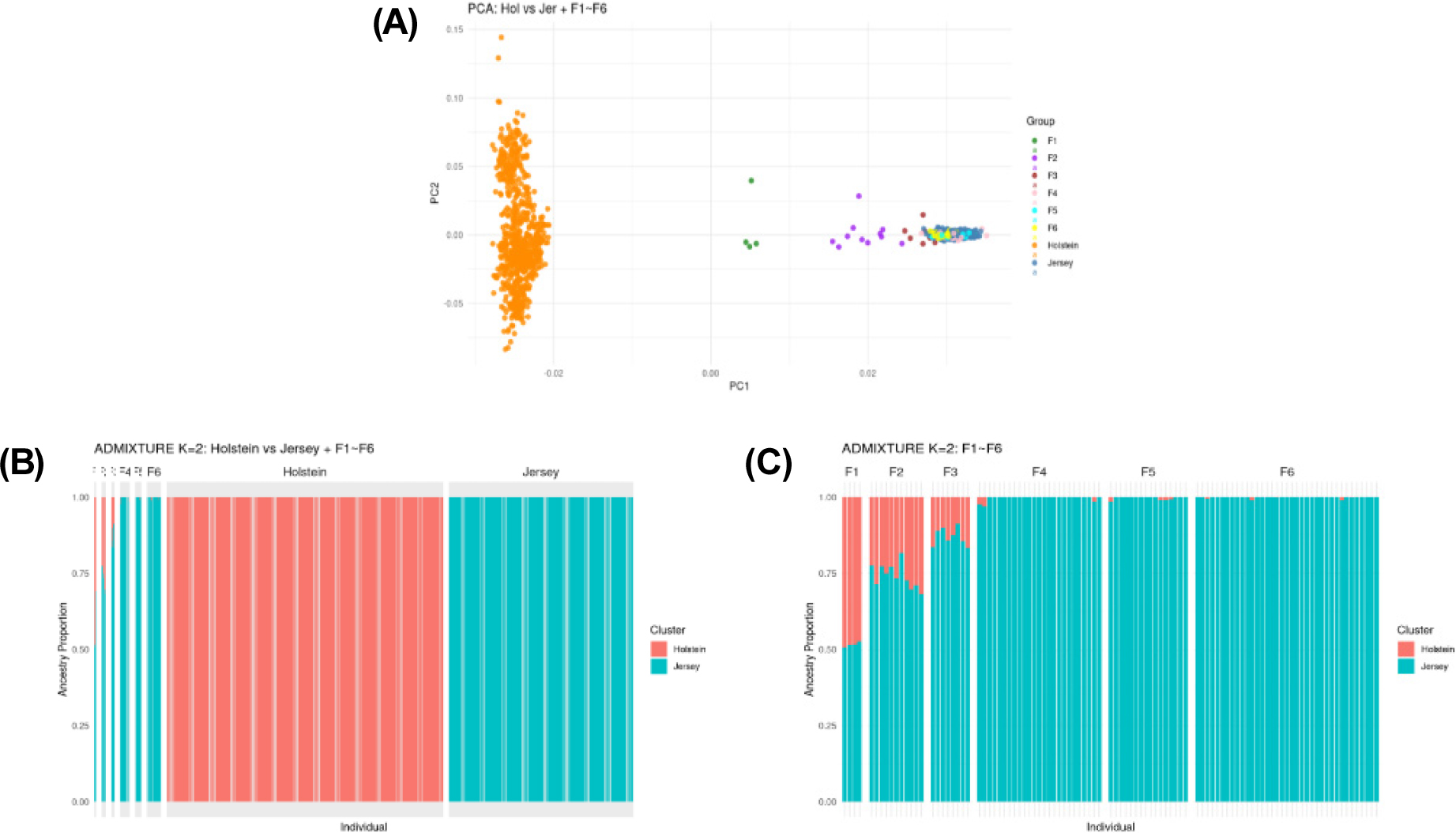
Fig. 3.
Genetic composition changes across F1 - F6 crossbred generations from repeated backcrosses of Jersey onto Holstein (A) Principal component analysis (PCA) including Holstein and Jersey reference populations and crossbred generations F1 - F6. (B) Genetic composition changes across F1 - F6 crossbreds (ADMIXTURE, K = 2). (C) Genetic composition changes in F1 - F6 crossbred generations resulting from repeated backcrosses of Jersey onto Holstein.
Table 3.
Changes in genetic composition based on ADMIXTURE analysis for crossbred generations (F1 - F6) resulting from repeated backcrosses of Jersey onto Holstein (K = 2).
| Breed | Holstein proportion | Jersey proportion |
| F1 (4) | 0.4481 | 0.5519 |
| F2 (11) | 0.2587 | 0.7413 |
| F3 (8) | 0.1296 | 0.8704 |
| F4 (25) | 0.0027 | 0.9973 |
| F5 (16) | 0.0024 | 0.9976 |
| F6 (34) | 0.0008 | 0.9992 |
The proportion of Jersey ancestry gradually increased across successive crossbred generations, from 55.2% in F1 to 99.7% in F4, reaching near-complete Jersey composition in F4 - F6. These results provide a genetic basis for classifying or registering offspring from the F4 generation onward as the Jersey breed.
F4 세대부터는 저지 비율이 99.7% 이상으로 나타나 reference 저지 집단과 구별하기 어려운 수준의 유전적 조성을 보였다. F5와 F6 세대 역시 각각 저지 99.8 - 99.9% 수준을 유지하여, 교잡 세대 누적에 따른 사실상 완전한 저지형 유전체 구성에 도달한 것으로 확인되었다(Fig. 3C).
이러한 결과를 통해 reference 집단의 유전적 비율을 기반으로 교잡 세대의 조성(ancestry)을 정량적으로 추정할 수 있었으며, F1 - F3 세대는 이론적 누적교배(backcross) 모델(F1: 50%, F2: 75%, F3: 87.5%)과 매우 유사한 유전적 비율을 보였다. 특히 F4 세대는 저지 유전 기여도가 약 99%로 증가하여, 이론적 기대치인 93.75% (15/16)보다 빠르게 저지형으로 수렴하는 경향을 보였다. F4에서 관찰된 홀스타인 기여도의 감소는 표본 수 제한과 저지 중심의 선택적 교배가 복합적으로 작용한 결과로 판단되며, 유전체 재조합에 따른 자연적 변동 가능성도 존재하므로 이를 확인하기 위해서는 추가 표본 확보가 필요하다. 이러한 패턴은 PCA에서도 동일하게 관찰되었으며, F4 이후 개체들은 reference 저지 집단과 거의 중첩되는 위치에 군집하여 사실상 저지형 유전 구조에 도달한 것으로 나타났다.
이와 같은 ADMIXTURE (supervised analysis) 결과는 reference로 설정된 홀스타인·저지 두 품종이 명확한 유전적 기준점을 제공하며, 교배 세대가 증가함에 따라 후대의 유전 조성이 어떻게 특정 품종 방향(저지)으로 고정되는지 정량적으로 보여준다. 특히 F4 이후의 개체는 유전적으로 저지 품종과 구별이 어려워, 실제 농가나 등록 체계에서 F4 이상을 저지 품종으로 분류하는 것이 타당함을 시사한다. 캐나다 Lactanet의 「Animal Pedigree Act (1985)」에서는 기초 조상(foundation breed)으로부터 7/8 (87.5%) 이상의 유전적 기여를 받은 경우 순종(purebred)으로 인정하고 있으며(Richardson and Van Doormaal, 2022), 미국 Council on Dairy Cattle Breeding (CDCB)은 유전체 기반 품종 조성 지표인 Breed Base Representation (BBR) 값이 94% 이상이면 순종으로 간주한다(CDCB, 2023). 또한 CDCB는 다세대 순종 혈통을 가진 개체라도 자연적 유전 변이로 인해 BBR 값이 94%까지 낮아질 수 있음을 보고하고 있으며, 이를 기준으로 BBR ≥ 94%를 순종 판정의 실질적 기준으로 제시한다. 더불어 누적교배(backcross) 이론에서도 F1 이후 3세대 동안 기초 품종과 반복 교배 시 유전 조성은 93.75%에 도달하여 ‘사실상 순종(practically purebred)’으로 인정되며, 5세대 이상의 backcross (96.9% 이상)를 거치면 공식적인 순종으로 분류할 수 있음이 제시되어 있다. 이러한 기준과 비교했을 때 본 연구에서 관찰된 F4 - F6 세대의 저지 유전 기여도(약 99%)는 교잡 세대가 저지형으로 안정적으로 고정되고 있음을 뒷받침한다.
다만, 본 연구에서 F4 이상의 개체 수가 충분하지 않기 때문에, 산업적·유전적 관점에서 F4 세대가 저지 품종으로 분류 가능한 최종 기준점인지, 혹은 F5 이후가 더 적절한지에 대해서는 향후 더 많은 표본을 활용한 추가 검증이 필요하다. 그럼에도 불구하고 본 연구에서 얻어진 유전체 기반 추정 값은 국제적으로 통용되는 순종 인정 기준(87.5 - 94% 이상)을 크게 상회하는 수준으로 수렴하였으며, 누적교배를 통한 저지혈통 고정이 빠르게 일어날 수 있음을 시사한다.
Conclusion
본 연구는 홀스타인과 저지를 reference 집단으로 활용하여 국내 한우·홀스타인·저지 및 F1 - F6 교잡 세대의 유전적 구조를 PCA와 supervised ADMIXTURE 분석으로 평가하였다. 분석 결과, 세 품종은 뚜렷하게 구분되는 독립적 유전 집단을 형성하였으며, 교잡 세대는 세대가 진행될수록 저지 기여도가 점진적으로 증가하였다. 특히 F4 세대 이후에는 저지 ancestry가 약 99% 수준에 도달하여 순종 판정의 국제 기준(87.5 - 94%)을 크게 상회하였다. 이는 누적교배를 통해 저지형 유전 구조가 빠르게 고정될 수 있음을 보여준다. 다만, F4 이상의 표본 수가 제한적이므로, F4를 최종 품종 분류 기준으로 확정하기 위해서는 추가 검증이 필요하다. 본 연구는 국내 저지 개체의 유전적 기반을 규명하고, 교잡 개체의 품종 판정 및 혈통 관리에 활용 가능한 과학적 근거를 제공하였으며, 향후 품종 등록, 교배 전략, 유전자원 보존 정책 수립에 중요한 참고 자료가 될 것으로 기대된다.